Класс: geneont
Найдите условия, которые являются предками заданного понятия Генной онтологии (GO)
AncestorIDs = getancestors(GeneontObj, ID)
[AncestorIDs, Counts]
= getancestors(GeneontObj, ID)
... = getancestors(..., 'Height', HeightValue,
...)
... = getancestors(..., 'Relationtype', RelationtypeValue,
...)
... = getancestors(..., 'Exclude', ExcludeValue,
...)
AncestorIDs = getancestors(GeneontObj, ID)GeneontObj поисковых запросов, объект geneont, для ИДУТ условия, которые являются предками ПОЙТИ термина (терминов), заданного ID, который является ПОЙТИ идентификатором термина или вектором идентификаторов. Это возвращает AncestorIDs, вектор ИДУТ идентификаторы термина включая ID. ID является неотрицательным целым числом или вектором, содержащим неотрицательные целые числа.
[ также возвращает число раз, которым найден каждый предок. AncestorIDs, Counts]
= getancestors(GeneontObj, ID)Counts является вектор-столбцом с тем же числом элементов как условия в GeneontObj.
Возвращаемое значение Counts полезно, когда вы соответствуете количествам в генных исследованиях обогащения. Для получения дополнительной информации смотрите Генное Обогащение Онтологии в Данных Микромассивов.
... = getancestors(..., 'PropertyName', PropertyValue, ...) getancestors с дополнительными свойствами, которые используют имя свойства / пары значения свойства. Можно задать одно или несколько свойств в любом порядке. Каждый PropertyName должен быть заключен в одинарные кавычки и нечувствительный к регистру. Это имя свойства / пары значения свойства следующие:
... = getancestors(..., 'Height', поисковые запросы через конкретное количество уровней, HeightValue,
...)HeightValue, в генной онтологии. HeightValue является положительным целым числом. Значением по умолчанию является Inf.
... = getancestors(..., 'Relationtype', поиски заданных типов связей, RelationtypeValue,
...)RelationtypeValue, в генной онтологии. RelationtypeValue является вектором символов. Выбором является 'is_a', 'part_of' или 'both' (значение по умолчанию).
... = getancestors(..., 'Exclude', средства управления, исключая ExcludeValue,
...)ID, исходный запрошенный термин (термины), от вывода AncestorIDs, если термин не был достигнут при поиске генной онтологии. Выбором является true или false (значение по умолчанию).
GeneontObj | Объект geneont, такой, как создано функцией конструктора geneont. |
ID | ПОЙДИТЕ идентификатор термина или вектор идентификаторов. |
HeightValue | Положительное целое число, задающее количество уровней, чтобы искать вверх в генной онтологии. |
RelationtypeValue | Вектор символов, задающий типы связей, чтобы искать в генной онтологии. Выбор:
|
ExcludeValue | Средства управления, исключая ID, исходный запрошенный термин (термины), от вывода AncestorIDs, если термин не был достигнут при поиске генной онтологии. Выбором является true или false (значение по умолчанию). |
AncestorIDs | Вектор ИДЕТ идентификаторы термина включая ID. |
Counts | Вектор-столбец с тем же числом элементов как условия в GeneontObj, указывая на число раз каждый предок найден. |
Загрузите текущую версию базы данных Gene Ontology с сети в объект geneont в MATLAB.
GO = geneont('LIVE', true)Программное обеспечение MATLAB создает объект geneont и отображает количество условий в базе данных.
Gene Ontology object with 24316 Terms.
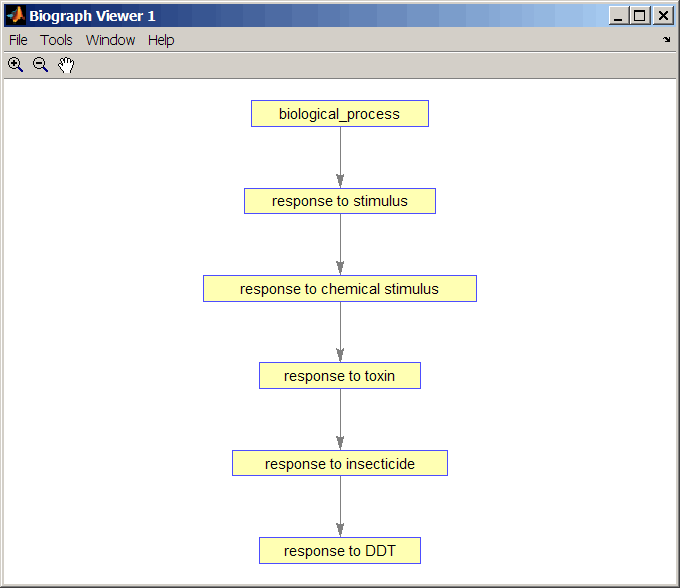
Получите предков Генного понятия Онтологии с идентификатором 46680.
ancestors = getancestors(GO,46680)
ancestors =
8150
9636
17085
42221
46680
50896Создайте зависимую Генную Онтологию.
subontology = GO(ancestors) Gene Ontology object with 6 Terms.
Создайте и отобразите отчет зависимых Генных условий Онтологии, который включает ПОЙТИ идентификатор и имя.
rpt = get(subontology.terms,{'id','name'})
[ 8150] 'biological_process'
[ 9636] 'response to toxin'
[17085] [1x23 char]
[42221] [1x29 char]
[46680] 'response to DDT'
[50896] [1x20 char]
Просмотрите отношения зависимой Генной Онтологии при помощи метода getmatrix, чтобы создать матрицу связи, чтобы передать функции biograph.
cm = getmatrix(subontology); BG = biograph(cm, get(subontology.terms, 'name')); view(BG)
goannotread | num2goid | term